
宏基因组二代测序(mNGS)已被广泛应用于感染性疾病的病原检测。然而,呼吸系统感染具有特殊性:病原组成复杂、标本类型选择多样、存在感染与定植、不同标本类型结果解读原则不尽相同等。为规范临床送检适应证,选择合适的送检标本以及恰当地解读报告,特组织专家对上述问题进行讨论并撰写专家共识,以期为呼吸系统感染中mNGS技术临床应用及报告解读提供专业的指导和帮助。

版权归中华医学会所有。
未经授权,不得转载、摘编本刊文章,不得使用本刊的版式设计。
除非特别声明,本刊刊出的所有文章不代表中华医学会和本刊编委会的观点。
呼吸系统感染是造成全球死亡人数最多的一类感染。2019年世界疾病负担研究学会的数据显示[1],下呼吸道感染(LRTIs)发病率和病死率在成人和儿童中位居第4位,2019年死亡人数达260万。呼吸系统感染的病原体种类繁多,病原诊断困难,只有通过快速精准的病原体判断,并进行针对性的抗感染治疗,才能达到最佳的临床预后[2]。虽然近年来分子生物学方法在感染性疾病病原检测中表现突出,但仍有50%左右的呼吸系统感染无法明确病原体[3,4]。
宏基因组二代测序(mNGS)通过对临床标本进行宏基因组测序,可以无偏向性地检出标本中的多种病原微生物(包括病毒、细菌、真菌和寄生虫),目前已被广泛应用于临床感染性疾病的病原检测,越来越多的临床研究及特殊病原体感染案例报道(特别是少见、苛养病原体)肯定了mNGS在感染性疾病辅助诊断中的价值[5,6],也不乏在呼吸系统感染中应用的研究[7,8,9,10]。然而,目前临床送检适应证不明,检测质量参差不齐,报告解读也缺乏规范。不同于无菌腔隙,呼吸系统与外界相通,存在正常菌群,微生物组成尤为复杂,定植菌与感染菌的鉴别困难;不同呼吸系统感染类型优选标本类型也不同,不同的标本类型检测结果解读原则不尽相同,故呼吸系统mNGS临床应用及报告解读需要更专业的指导。目前我国已发表多个mNGS专家共识[11,12,13,14,15,16],但对临床上应用越来越广泛且结果解读难度较高的呼吸系统感染缺少专门介绍。为提高mNGS在呼吸系统感染病原诊断中的质量,规范临床送检适应证,选择合适的送检标本类型以及恰当解读报告,特邀请感染病学、呼吸病学、临床微生物学及医院感染管理等领域的专家共同编写制订此共识。此共识适用于上呼吸道感染(病毒感染等)、LRTIs(肺炎、肺脓肿、支气管扩张伴感染等)和胸腔感染。共识内容旨在为临床样品送检和解读提供参考,不作为临床诊断标准流程。
以下送检推荐,建议在送检mNGS的同时送检传统微生物检测。
推荐1:疑似LRTIs的危重症患者,建议送检mNGS。
由于现有常规微生物检测方法敏感度低、检测时间长及病原谱窄等因素的限制,LRTIs病原检出率低。重症LRTIs患者若得不到及时有效治疗,病情可迅速进展,甚至危及生命。重症肺炎中mNGS较传统方法病原检出率更高,可降低重症肺炎病死率[17,18]。
推荐2:免疫功能抑制患者的呼吸系统感染,建议送检mNGS。
免疫抑制患者发生呼吸系统感染时,致病病原体较免疫正常患者更为复杂,且起病隐匿,进展快速,预后差,病死率高,故应特别重视,尽早明确病原学诊断。免疫抑制按机制主要分为粒细胞减少或功能障碍、体液免疫缺陷和细胞免疫缺陷三种类型,某些患者可能存在联合免疫抑制[19]。在免疫抑制患者中,mNGS检测到的病原体更多,临床符合率高,能发现更多的真菌、病毒以及混合感染,如巨细胞病毒(CMV)合并耶氏肺孢子菌[8,20]。
推荐3:疑似慢性肺部感染或难治性感染,且既往治疗效果不佳时,建议送检mNGS。
普通医疗机构对于慢性感染病原体及特殊病原体缺乏有效的检测手段。通常这类病原体检测耗时长、敏感度低或完全无法通过常规的培养及免疫学手段进行确诊。多个临床研究显示,mNGS在分枝杆菌[结核分枝杆菌(MTB)、非结核分枝杆菌(NTM)]、真菌(毛霉、曲霉)和厌氧菌等病原体检出优于传统培养[21,22,23]。
推荐4:疑似呼吸道感染暴发且病原体不明,建议送检mNGS。
呼吸道感染暴发应采取准确、快速、全面的方法以尽快明确病原体,医院感染管理科、疾病预防控制中心等部门方可根据病原体采取有效的防控措施。对于新发病原体,mNGS具有传统培养及靶向分子诊断技术所不具备的优势[24,25]。
推荐5:通过有创性操作获取的组织标本,如经皮肺穿刺组织、经支气管镜肺活检组织(TBLB)及经超声支气管镜淋巴结穿刺活检组织(EBUS-TBNA)等,建议送检mNGS。
经皮肺穿刺活检术、TBLB、EBUS-TBNA需在CT、X线透视或超声引导下进行,能够直接取到病变组织。但是,标本采集操作难度高、标本重复采集可能性低,目前包括组织病理、肺组织涂片、培养及其他分子生物学检查均有各自的局限性。因此,送检mNGS可提高病原诊断敏感度,通过不同检测方法组合,提高病原诊断率,尽早进行目标性治疗。
推荐6:怀疑厌氧菌引起的肺脓肿、坏死性肺炎或其他肺部感染,建议采集避免口腔菌群污染的标本(如下呼吸道标本、经皮穿刺肺活检组织及胸腔积液),送检mNGS。
厌氧菌培养需要绝对厌氧环境,且通常为合并感染,故常规培养阳性率低,由混合口腔厌氧菌所致慢性肺脓肿并不少见。多项研究[26,27,28]发现,mNGS在厌氧菌诊断中具有优势,通过mNGS证实了如以微小单胞菌、具核梭杆菌等为主的混合厌氧菌感染病例。
呼吸道感染标本类型的选择首先需考虑从原发感染部位采集,LRTIs更为复杂,肺部病灶部位、形态、大小、咳痰质量、有创操作耐受情况等均会影响选取最合适的标本类型。常见考虑送检的标本类型、采集要求、保存条件及特殊说明见表1。以下送检推荐,建议在送检mNGS的同时送检传统微生物检测。
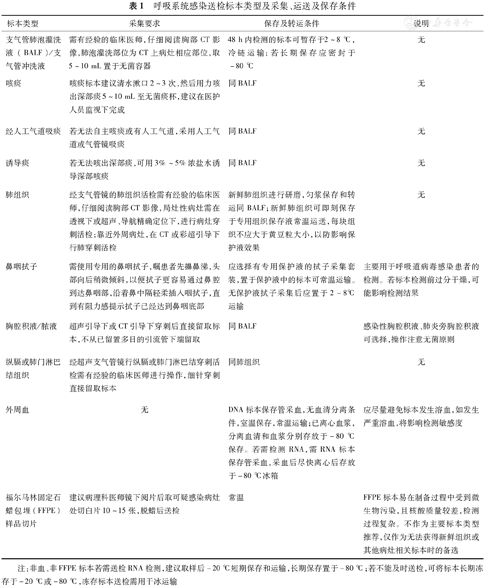
呼吸系统感染送检标本类型及采集、运送及保存条件
呼吸系统感染送检标本类型及采集、运送及保存条件
| 标本类型 | 采集要求 | 保存及转运条件 | 说明 |
|---|---|---|---|
| 支气管肺泡灌洗液(BALF)/支气管冲洗液 | 需有经验的临床医师,仔细阅读胸部CT影像,肺泡灌洗部位为CT上病灶相应部位,取5~10 mL置于无菌容器 | 48 h内检测的标本可暂存于2~8 ℃,冷链运输;若长期保存应密封于-80 ℃ | 无 |
| 咳痰 | 咳痰标本建议清水漱口2~3次,然后用力咳出深部痰5~10 mL至无菌痰杯,建议在医护人员监视下完成 | 同BALF | 无 |
| 经人工气道吸痰 | 若无法自主咳痰或有人工气道,采用人工气道或气管镜吸痰 | 同BALF | 无 |
| 诱导痰 | 若无法咳出深部痰,可用3%~5%浓盐水诱导深部咳痰 | 同BALF | 无 |
| 肺组织 | 经支气管镜的肺组织活检需有经验的临床医师,仔细阅读胸部CT影像,局灶性病灶需在透视下或超声、导航精确定位下,进行病灶穿刺活检;靠近外周病灶,在CT或彩超引导下行肺穿刺活检 | 新鲜肺组织进行研磨,匀浆保存和转运同BALF;新鲜肺组织可即刻保存于专用组织保存液常温运送,每块组织不应大于黄豆粒大小,以防影响保护液效果 | 无 |
| 鼻咽拭子 | 需使用专用的鼻咽拭子,嘱患者先擤鼻涕,头部向后稍微倾斜,以便拭子更容易通过鼻腔到达鼻咽部,沿着鼻中隔轻柔插入咽拭子,直到有阻力感提示拭子已经达到鼻咽底部 | 应选择有专用保护液的拭子采集套装,置于保护液中的标本可常温运输。无保护液拭子采集后应置于2~8℃运输 | 主要用于呼吸道病毒感染患者的检测。若标本检测前过分干燥,可能影响检测结果 |
| 胸腔积液/脓液 | 超声引导下或CT引导下穿刺后直接留取标本,不从已留置多日的引流管下端留取 | 同BALF | 感染性胸腔积液、肺炎旁胸腔积液可选择,操作注意无菌原则 |
| 纵膈或肺门淋巴结组织 | 经超声支气管镜行纵膈或肺门淋巴结穿刺活检需有经验的临床医师进行操作,细针穿刺直接留取标本 | 同肺组织 | 无 |
| 外周血 | 无 | DNA标本保存管采血,无血清分离条件,室温保存,常温运输;已离心血浆,分离血清和血浆分别存放于-80 ℃保存。若需检测RNA,需RNA标本保存管采血,采血后尽快离心后存放于-80 ℃冰箱 | 应尽量避免标本发生溶血,如发生严重溶血,将影响检测敏感度 |
| 福尔马林固定石蜡包埋(FFPE)样品切片 | 建议病理科医师镜下阅片后取可疑感染病灶处切白片10~15张,脱蜡后送检 | 常温 | FFPE标本易在制备过程中受到微生物污染,且核酸质量较差,检测过程复杂。不作为主要标本类型推荐,仅作为无法获得新鲜组织或其他病灶相关标本时的备选 |
注:非血、非FFPE标本若需送检RNA检测,建议取样后-20 ℃短期保存和运输,长期保存置于-80 ℃;若不能及时送检,可将标本长期冻存于-20 ℃或-80 ℃,冻存标本送检需用干冰运输
推荐7:怀疑感染的肺部弥漫性病变,建议首选支气管肺泡灌洗液(BALF);若无法耐受有创性检查,建议选择诱导痰、咳痰或者经上呼吸道吸痰标本。
对于LRTIs,最常见送检标本是BALF和痰。BALF直接取自下呼吸道,相较于痰标本黏稠、不均匀以及易被口咽部定植菌影响的短板,BALF直接取自下呼吸道,更推荐其作为LRTIs的首选标本。然而,收集BALF需进行有创的纤维支气管镜检查,需考虑患者耐受情况,咳痰、诱导痰或经上呼吸道吸痰标本可作为一种替代标本。虽然没有mNGS在同一患者的BALF与痰标本检出阳性率及临床符合率的研究,多个研究结果也证实了BALF在检出各种病原体中的优势[29]。
推荐8:怀疑病毒性LRTIs者,建议同时送检下呼吸道标本进行DNA+RNA检测。
病毒性肺炎的常见呼吸道病原体可分为RNA病毒及DNA病毒,以RNA病毒为主。常见的RNA病毒包括流感病毒、副流感病毒、鼻病毒、呼吸道合胞病毒、人冠状病毒、人偏肺病毒和肠道病毒(如柯萨奇病毒、埃可病毒)等,DNA病毒常见腺病毒、CMV、单纯疱疹病毒等[30,31,32]。行DNA和RNA检测所需标本保存条件有所区别,RNA容易降解,对标本的采集、保存和运输条件相对苛刻。当不能排除RNA病毒感染时,应考虑行RNA流程检测。DNA+RNA检测流程可保证对包括RNA病毒在内的全部微生物类别进行检测覆盖。
推荐9:疑似病毒性LRTIs者,若无法获得下呼吸道标本,建议采集鼻咽拭子或外周血送检mNGS。
病毒性肺炎通常无明显咳痰,只有28%~33.7%的新型冠状病毒肺炎患者可以采集到痰标本[33,34]。而鼻咽拭子在流感、新型冠状病毒肺炎中被证明具有很好的诊断价值[35]。另有研究发现,血液标本在部分病毒的鉴定上优于BALF[29]。外周血检测作为一项无创、简单及快速的检测方式,相对于BALF、肺组织活检等有创检查方法极具优势[24]。所以如果无法获得下呼吸道标本,可以考虑采取上呼吸道标本或者外周血标本进行检测。
推荐10:对于肺部外周性病灶、局限性病灶或纵膈、纵膈/肺门淋巴结肿大,应根据病灶的特点,个体化选择有创性操作方式获取组织送检。
如果传统微生物检测方法阴性,经验性抗感染效果欠佳的局限性病灶、外周型结节团块病灶或纵膈/肺门淋巴结肿大,建议行有创性检查。需有经验的临床医师综合考虑,根据病灶大小、位置、与支气管位置、周围血管分布以及操作者对采样技术的熟练程度,分析操作的可行性和评估可能不良反应,选择更适合、活检成功把握度高的方法,如超声、CT或导航直视下操作可直达病变部位,精确取材可显著提高mNGS的检出阳性率[36,37]。肺组织标本较BALF人源背景序列高,虽然目前无相关研究比较同一部位BALF和肺组织mNGS结果,既往的研究结果和经验显示,对于多种病原体,BALF较肺组织敏感度更高[38]。以适当技术进行人源核酸去除可有效提高整体检测敏感度。同时建议新鲜组织行mNGS,虽然目前也有福尔马林固定石蜡包埋(FFPE)标本行mNGS,但由于实验流程复杂,对DNA和RNA易造成损害。虽然FFPE可长期保存,但却很难被有效地处理和分析,另外易被如真菌、NTM及细菌等环境微生物污染。
推荐11:对于疑似肺部感染而无法取得呼吸道标本患者,建议采集外周血送检mNGS。
除了呼吸道感染继发血流感染的情况外,肺部病原凋亡后的细胞游离DNA依然可能释放到外周血中被检测到。当前对于外周血mNGS检测提示呼吸道感染责任病原的可行性缺乏大规模临床研究的支持,但是一些研究结果提示其可行性[39]。在这类小规模研究中[29,40,41],对于呼吸道感染的患者,外周血中病原检测阳性率为35%~86.7%,造血干细胞移植患者疑似侵袭性曲霉感染患者中外周血mNGS检测的敏感度为51%,对于非曲霉侵袭性真菌感染的敏感度达79%[20]。
推荐12:对于肺部病灶疑似为全身疾病累及的患者,建议采集其他局部病灶作为次选标本,送检mNGS。
某些病原体可导致全身多部位感染,如分枝杆菌、隐球菌、诺卡菌等,肺部病灶作为全身感染的一个部分,若临床上考虑一元论的可能性大,但又无法明确诊断时,可根据获得标本的难易程度及诊断价值,取多个病灶行mNGS检测,检测结果符合临床特征及胸部影像,可作为辅助诊断肺部病灶的依据。
mNGS具有无偏向性检出的特性,能检出临床标本中所有的微生物,而呼吸道感染有多种可能检测的标本,因其定植菌、微生物比例、空间异质性等存在差异,会对临床解读造成困惑。临床医师需密切结合患者的发病过程、实验室检查、影像学等结果,判断检出病原体是否符合临床诊断,并可进一步通过其他技术进行交叉验证。另外需指出,测序平台、流程、深度有所不同,该部分解读对大部分情况有参考价值,不除外特殊情况不符合者。
鼻咽拭子、痰、BALF属于呼吸道标本,能较好地反映上呼吸道或下呼吸道菌群状态,这类标本通常能检出多种微生物,其中多数可能为呼吸道常见定植菌。临床医师需在mNGS检出的众多微生物中筛选可能的致病菌,筛选过程参考的因素包括微生物自身特性(致病性、条件致病、定植及传染性等)、序列数(绝对序列数和占此标本中的相对比例)、特殊环境暴露史或病史、临床症状及检查等。序列数是指二代测序中检测到的短DNA序列的条数,序列数大小与标本中该微生物的数量正相关,但同时序列数也受到测序数据量、人源数据占比、物种基因组大小及基因组特异性序列比例等因素的影响。在不同的标本类型中,同样的序列数可能有截然不同的解读方式[42]。呼吸道标本检出的微生物相对复杂,通常会检出序列数较多的定植菌,此时需要考虑其相对丰度,即该物种占这份标本中所有微生物的比例。
如何有效精准地解读呼吸道标本mNGS结果已成为临床医师关心的重点问题,呼吸系统标本mNGS检测结果解读需遵循以下原则:(1)检出结果需结合临床表现、实验室检查、及胸部影像学;(2)检出结果需结合其他传统微生物报告,并通过其他检测技术进行交叉验证;(3)结合检出微生物的种类、特异性序列数级相对丰度判断其为致病菌、定植菌还是背景菌;(4)若单一标本无法判定是否致病微生物,有条件情况下可结合多个不同类型标本的检测结果判断。表2详述了不同类型标本检出不同微生物的临床意义。

不同类型标本宏基因组二代测序检出微生物的临床意义
不同类型标本宏基因组二代测序检出微生物的临床意义
| 病原体 | BALF | 痰 | 经皮肺穿刺组织 | 经气管镜活检肺组织 | 胸腔积液/脓液 | 鼻咽拭子 | FFPE | 外周血 | ||
|---|---|---|---|---|---|---|---|---|---|---|
| 细菌 | ||||||||||
| 肺炎链球菌 | + | + | ++ | ++ | + | ± | ± | + | ||
| 溶血性链球菌 | ± | ± | ++ | + | + | ± | ± | + | ||
| 非溶血性链球菌 | ± | ± | + | + | + | ± | ± | ± | ||
| 奈瑟菌属(非淋病) | ± | ± | + | + | + | ± | ± | ± | ||
| 莫拉菌属 | ± | ± | + | + | + | ± | ± | ± | ||
| 嗜血杆菌属 | ± | ± | + | + | + | ± | ± | ± | ||
| 普雷沃菌属 | ± | ± | + | + | + | ± | ± | ± | ||
| 韦荣球菌属 | ± | ± | + | + | + | ± | ± | ± | ||
| 罗氏菌属 | ± | ± | + | + | + | ± | ± | ± | ||
| 消化链球菌属 | ± | ± | + | + | + | ± | ± | ± | ||
| 放线菌属 | ± | ± | + | + | + | ± | ± | ± | ||
| 弯曲菌属 | ± | ± | + | + | + | ± | ± | ± | ||
| 凝固酶阴性葡萄球菌 | ± | ± | + | ± | ± | ± | ± | ± | ||
| 金黄色葡萄球菌 | + | ± | ++ | + | + | ± | ± | + | ||
| 放线菌属 | + | ± | ++ | + | + | ± | ± | + | ||
| 诺卡菌属 | + | + | ++ | + | + | ± | ± | + | ||
| 鲍曼不动杆菌 | + | + | + | + | + | ± | + | + | ||
| 铜绿假单胞菌 | + | + | ++ | + | + | ± | + | + | ||
| 肺炎克雷伯菌 | + | + | ++ | + | + | ± | + | + | ||
| 大肠埃希菌 | + | + | ++ | + | + | ± | + | + | ||
| 肠球菌属 | + | ± | ++ | + | + | ± | + | |||
| 嗜麦芽窄食单胞菌 | + | + | + | + | + | ± | + | + | ||
| 分枝杆菌 | ||||||||||
| 结核分枝杆菌 | ++ | ++ | ++ | ++ | ++ | ± | ++ | ++ | ||
| 致病性NTM | ++ | ++ | ++ | ++ | + | ± | + | ± | ||
| 非致病性NTM | ± | ± | ± | ± | ± | ± | ± | ± | ||
| 病毒 | ||||||||||
| 单纯疱疹病毒 | ++ | + | ++ | ++ | + | + | ± | + | ||
| 水痘带状疱疹病毒 | ++ | + | ++ | ++ | + | + | ± | + | ||
| 腺病毒 | ++ | + | ++ | ++ | + | + | ± | + | ||
| 呼吸道合胞病毒 | ++ | + | ++ | ++ | + | + | ± | + | ||
| EB病毒 | ++ | + | ++ | ++ | + | + | + | + | ||
| 巨细胞病毒 | ++ | + | ++ | ++ | + | + | ± | + | ||
| 甲、乙型流感病毒 | ++ | + | ++ | ++ | + | + | ± | + | ||
| 禽流感病毒 | ++ | + | ++ | ++ | + | + | ± | + | ||
| 冠状病毒 | ++ | + | ++ | ++ | + | + | ± | + | ||
| 真菌 | ||||||||||
| 念珠菌属 | ± | ± | + | ± | + | ± | ± | + | ||
| 耶氏肺孢子菌 | ++ | ++ | ++ | ++ | ± | ++ | ± | ++ | ||
| 隐球菌 | ++ | + | ++ | ++ | ± | ± | ++ | ++ | ||
| 曲霉 | + | + | ++ | + | ± | ± | + | + | ||
| 毛霉 | ++ | ++ | ++ | ++ | + | ± | + | + | ||
| 赛多孢子菌 | + | + | ++ | ++ | + | ± | + | + | ||
| 马尔尼菲篮状菌 | ++ | ++ | ++ | ++ | ++ | ± | + | + | ||
| 组织胞浆菌 | ++ | ++ | ++ | ++ | ++ | ± | + | + | ||
| 寄生虫 | ||||||||||
| 肺吸虫 | ++ | ± | ++ | ++ | + | ± | + | ± | ||
| 非典型病原体 | ||||||||||
| 嗜肺军团菌 | ++ | + | ++ | ++ | ± | ± | + | ++ | ||
| 肺炎支原体 | + | + | ++ | ++ | + | ± | + | ++ | ||
| 鹦鹉热衣原体 | ++ | ++ | ++ | ++ | + | ± | ++ | ++ | ||
| 高致病性传染性病原体 | ||||||||||
| 鼠疫杆菌 | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ||
| 霍乱弧菌 | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ||
| 布鲁菌 | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ||
| 炭疽芽孢杆菌 | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ||
| 百日咳杆菌 | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ||
| 破伤风杆菌 | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ||
| 苍白螺旋体 | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ||
| HIV | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ||
| 狂犬病病毒 | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ||
| 登革热病毒 | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ||
| 乙脑病毒 | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ||
| 高致病性禽流感病毒 | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ||
| SARS病毒 | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ||
| 新型冠状病毒 | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ||
| 埃博拉病毒 | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ||
| 新疆出血热病毒 | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ||
| Flexal病毒 | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ++ | ||
注:BALF.支气管肺泡灌洗液;FFPE.福尔马林固定石蜡包埋;NTM.非结核分枝杆菌;HIV.人类免疫缺陷病毒;±表示意义不明;+表示可能有意义;++表示有意义
推荐13:若痰标本或BALF检出上呼吸道常见定植微生物,如草绿色链球菌、奈瑟菌属、嗜血杆菌属、普雷沃菌属、韦荣球菌属、罗氏菌属、凝固酶阴性葡萄球菌、肠球菌属、念珠菌属等,考虑定植可能大。
健康人群鼻咽、口咽部存在定植微生物群[43],但其中一些微生物在健康宿主中也可在特定情况下致病,如由于既往病毒感染造成的损害、宿主免疫下降或呼吸道上皮屏障的物理破坏。根据标本来源、微生物的量以及白细胞数量来区分定植和感染是很关键的。对于mNGS报告解读,需熟悉定植病原体的种类。
推荐14:若痰标本或BALF检出不存在或很少存在于口腔的病原体,如嗜肺军团菌、衣原体、百日咳博德特氏菌、白喉棒状杆菌等,考虑致病微生物可能大。
常见呼吸道确定的致病病原体如MTB、肺炎支原体、沙眼衣原体、肺炎衣原体、百日咳博德特氏菌、军团菌属、耶氏肺孢子菌、诺卡菌属、组织胞浆菌、球孢子菌属、隐球菌属、皮炎芽生菌及病毒等[43],此类病原体一旦检出即使序列数少仍需考虑致病微生物可能大。另有一些少见的呼吸道确定病原体如土拉弗朗西斯菌、鼠疫耶尔森菌、类鼻疽伯克霍尔德菌、贝纳柯克斯体、鹦鹉衣原体、布鲁菌、沙门氏菌属、多杀巴斯德菌、水痘带状疱疹病毒、寄生虫。但仍需注意某些环境和水源性微生物,军团菌等致病菌也存在水源污染可能,判读需谨慎。
推荐15:若呼吸道标本检出结核分枝杆菌复合群(MTBC,包括MTB、卡内蒂分枝杆菌、非洲分枝杆菌和牛分枝杆菌),即使序列数极少,仍需考虑其为致病微生物的可能。
MTB DNA提取困难,而污染的可能性低,有研究主张在种或属水平上至少有1条特异性序列时被认为是阳性[2,44]。当mNGS报告中检出序列数较低的MTB时,可要求检测机构对检出特异性序列进行复核,或对原始标本进行其他方法验证以确定检出的真实性。例如送检BALF标本,mNGS报告出1条MTB序列时,也应高度重视:一方面可要求报告出具方回溯检测流程和质控,对原始标本进行PCR验证;另一方面可加做Xpert MTB/RIP等MTB特异性检测方式进行确认。MTBC中4种分枝杆菌的基因组序列具有很高的相似性,因此建议关注MTBC特异性序列数,而不是某单一物种的特异性序列[37]。Miao等[23]将MTB特异性序列数(属或种水平)在细菌列表中排名前20位时被定义为阳性。因此,MTB在检出至少1条特异性序列时,即有可能提示感染,建议结合临床证据来解读,如是否有影像学证据支持。
推荐16:若呼吸道标本检出NTM,需结合所检出分枝杆菌属排名情况及种的类别,如常见致病的鸟胞分枝杆菌复合群、脓肿分枝杆菌复合群、堪萨斯分枝杆菌,考虑其为致病微生物的可能。
由于医院-实验室环境污染[45]和低产出率[46]的平衡,有研究认为NTM的特异性序列数(属或种水平)在细菌列表前10位时被定义为阳性[23]。临床经验建议NTM检出10条以上特异性序列时,考虑感染可能性较大,仅有极少量检出序列时存在标本污染或定植的可能性。
推荐17:若呼吸道标本检出隐球菌属、曲霉属、毛霉属及其他丝状真菌,若检出序列数较低,需结合影像学、血清学、组织病理学等考虑其为致病微生物的可能。
真菌(主要包括曲霉属、毛霉属、隐球菌属与双相真菌等)通常基因组较大,并且存在较厚的细胞壁,同样存在核酸提取效率低的情况。即使前期进行了破壁处理,其检出的特异序列数相对其他微生物仍然较少。因此对于真菌的鉴定,有研究认为,mNGS检出真菌(种水平)的特异性序列数是任何其余真菌的5倍以上,判断为阳性[4,23]。由于不同检验机构mNGS流程、方法存在差异,检出结果有一定误差。对于上述检出较为困难的微生物,除了结合临床证据,建议和其他微生物检出技术交叉验证,如特异引物的PCR等分子生物学检测、GM试验等血清学试验等,进一步确认或排除病原微生物。如果临床有疑似难检出的病原体感染,在报告中未列举,建议追溯原始数据进行复核,在报告阈值之外考虑可能的原始检出病原体。
推荐18:医院获得性肺炎/呼吸机相关肺炎(HAP/VAP)患者若检出院内感染病原体,如鲍曼不动杆菌、铜绿假单胞菌、肺炎克雷伯菌及嗜麦芽窄食单胞菌等条件致病菌,需要将检出序列数、相对丰度与机械通气、临床信息、影像学证据综合考虑是否为致病微生物。
对HAP/VAP患者进行mNGS,主要集中三个方面进行结果的判读:(1)如果某种病原体较其他病原体相对丰度有较大(数量级)优势,可能会是责任病原体。HAP/VAP患者气道和(或)人工气道易有不动杆菌属、假单胞菌属、嗜麦芽窄食单胞菌等定植,即使检出有较大丰度优势,仍需结合临床特点及影像学表现考虑是否为致病原;(2)如果检出相对丰度低,且患者无相关的临床表现,该检出是定植或污染的可能性大[47];(3)若在同时送检的呼吸道标本和外周血标本中检测到相同的病原,判断是致病原的可能性大。
推荐19:免疫功能抑制患者的呼吸系统感染检出的低毒力病原体,需考虑致病微生物可能大。
呼吸道定植病原体在免疫低下或呼吸道屏障功能破坏时,可能会由定植转为致病,如金黄色葡萄球菌、嗜麦芽窄食单胞菌、洋葱伯克霍尔德菌、铜绿假单胞菌、鲍曼不动杆菌、念珠菌属或部分病毒等。深部痰标本或BALF检出以上病原体,也需要重点关注并综合患者的临床表现和其他病原学检测手段综合判定。常见呼吸道感染病原体仍是免疫缺陷患者最常见的致病菌,在免疫缺陷患者和有基础性疾病患者呼吸道中检测到真菌如耶氏肺孢子菌、曲霉、隐球菌、马尔尼菲篮状菌等,DNA病毒如腺病毒、CMV及EB病毒等,RNA病毒中鼻病毒等,序列数及相对丰度较低时,仍需考虑为致病菌[48,49,50,51,52,53,54,55,56,57,58]。
推荐20:mNGS如检出高传染性或高致病性病原体,无论特异性序列数多少都应充分重视,需对检测结果进行复核以及使用其他检测技术验证。
强/烈性传染病病原体,指《中华人民共和国传染病防治法》中规定的甲类和乙类传染病病原体,大部分病毒为高传染性病原,符合《人间传染的病原微生物目录》[59]中的第一类和第二类规定。
如送检mNGS报告出高传染性疾病病原体,应根据当地卫生行政部门制定的报告程序上报,同时做好相应的防范隔离措施。对于人畜共患高致病性和高传染性病原体,如狂犬病病毒、布鲁菌及人感染高致病性禽流感病毒等,如有检出,除复核,并上报地方疾病预防控制中心进行验证,若确证试验阳性,按传染病要求上报系统。
推荐21:呼吸道标本若检出环境中广泛存在的微生物时,需考虑标本处理过程中的污染。
采样、检测过程可能受环境广泛存在微生物的影响,尤其对于这类病原体检出序列数及相对丰度较低时,污染来源可能性相对更大,需结合临床其他检测手段及患者临床表现来判断此病原体为责任病原体的可能性。如NTM中的很多菌种广泛存在于自然界中,当mNGS检出病原体种类较多,其中少见致病的NTM(如耻垢分枝杆菌、戈登分枝杆菌、蟾分支杆菌等)相对丰度及序列数相对较低,则需考虑环境污染可能。此外,军团菌、曲霉属及阿米巴等,也都广泛存在于自然界中的水、土壤和空气中,军团菌主要在人工水环境中居多,嗜肺军团菌是引起军团菌病的重要的菌种[60,61]。曲霉属的烟曲霉、黄曲霉及黑曲霉为主要致病菌。因此当有低序列数的非嗜肺军团菌和其他曲霉菌等检出时,最终都需要结合相关临床表现、影像学进行判读,同时有必要采用其他方法进行验证确诊。
推荐22:呼吸系统标本若检出大量口腔厌氧菌,需结合患者的病史、标本类型,必要时结合文献资料综合判读。
对于肺脓肿、坏死性肺炎患者,需考虑经由咽、口、鼻腔等途径吸入病原体。厌氧菌占肺脓肿病因的60%~80%,如具核梭杆菌、星状链球菌、脆弱拟杆菌、中间普雷沃菌、微小单胞菌、牙龈卟啉单胞菌、福赛斯坦纳菌及齿垢密螺旋体等[28,29,62,63,64],痰标本或BALF检出大量口腔厌氧菌,需结合病史、肺部影像学考虑是否为致病微生物,必要时进行其他类型标本验证;若经皮穿刺肺组织检出大量口腔厌氧菌,需考虑为致病病原体。
推荐23:若2种类型呼吸道标本或1种呼吸道标本与1种非呼吸道标本同时检出同一病原体,需考虑有临床意义。
临床应用中,常有同一患者多种类型标本同时检测的情况,如BALF与外周血,多标本检测为致病菌判断提供了更多参考信息,尤其对于呼吸道这类存在多种定植菌的标本鉴别价值大,若有一致检出,则需重点关注,不一致时需要结合其他因素综合分析[29,41,65]。
mNGS病原检测技术已经在临床上有了一定的应用,但是在实际应用中依然面临着一些挑战。
标本采集:目前标本的采集过程仍然缺乏统一的要求,如对于BALF的灌洗量、灌洗方式、回收方式及最佳送检区段等都缺乏针对mNGS检测方式的标准。而不同的标本采集方式及手法会显著影响到检测结果的可信度及临床意义。制订更为详细的标本采集规范和标本质量评估标准仍然具有挑战性。
检测流程:目前尚缺乏对mNGS的基本性能和参数的统一要求,不同检测机构的检测流程及检测性能可能存在较大差异,且对于同一术语不同检测机构的定义也可能存在差异[10,66],这给临床医师对于检测结果的解读会造成较大困难。相关部门及企业需协同制定更为完善的技术标准及要求。
检测结果与临床相结合:虽然mNGS技术对于传统病原学检测技术具有优势,但是仍然具有自身的局限性,其检测结果不宜作为唯一的临床感染性疾病诊断依据。检测结果的临床意义也需要结合患者的病史、用药史、免疫状态等进行综合分析。传统病原学检测技术依然是临床感染性疾病诊断的有效信息手段,也应得到充分合理的应用。各类检测相互交叉印证,可以获得更为准确可靠的病原学信息。
在感染性疾病诊疗领域,病原微生物耐药现象日益突出。全球约有100万人死于无法用普通抗菌药物治疗的细菌感染[67],控制细菌耐药性已经成为全球公共健康领域面临的一项重大挑战。目前临床和实验室最常用的细菌耐药检测方法为药物敏感性试验,其依赖于菌培养阳性结果,但不适用于难培养及非培养菌,且耗时较长。因此,很难满足重急症感染快速诊断和对症治疗的需求[68]。
mNGS辅助进行耐药基因检测,对临床上无法获得病原菌从而无法进行药敏试验的标本起到了很好的补充作用。但在实际应用过程中仍然存在诸多问题:基因型与表型分离;部分耐药性状源于单核苷酸突变或蛋白突变等,无法被现有临床mNGS检测流程识别;病原基因组测序覆盖度较低而出现漏检;耐药基因数据库不完善而无法满足部分耐药机理的检测;耐药基因无法区分具体基因组,明确微生物来源等。这些问题均会限制mNGS耐药检测的临床应用效果。
针对宏基因组耐药基因检测所面临的挑战,依赖于耐药基因数据库及mNGS技术的进一步发展。ARDB(https://ardb.cbcb.umd.edu/)及CARD(https://card.mcmaster.ca)等公共数据库涵盖了抗菌素耐药性基因和机制等信息,MUBII-TB-DB数据库提供特定物种及基因家族综合信息,通过对多个数据库的整合和对耐药机理的进一步研究,构建持续更新的综合数据库是后续的主要工作之一。同时,通过对耐药基因相关的耐药性状进行分级,可以获得更友好、更易读的检测结果;随着mNGS检测成本的不断降低,通过测序数据量的进一步加大,可以获得更为完整的优势菌的基因组覆盖度,能够获得可信度更高的检测结果。
除了临床用药的提示外,是否可以通过检出的耐药基因及毒力基因辅助责任病原菌的判定也值得进一步探索。有研究发现对于呼吸系统感染的人群,呼吸道耐药基因丰度分布具有显著差异,且耐药基因的表达与细菌分类群之间具有相关性,例如链球菌和莫拉菌与β-内酰胺耐药基因的表达呈正相关,而其他常见呼吸道细菌如奈瑟菌属,与多重耐药基因的表达呈正相关[69]。这为进一步探索通过对标本中耐药基因及毒力基因的相对丰度分布特点、对高毒力菌株的提示等,辅助对潜在责任病原菌的确定提供了可能。
对外周血、脑脊液等无菌体液而言,mNGS检测结果责任病原微生物的确定相对明确。但是,呼吸道作为开放体腔,定植大量条件致病微生物,对于责任病原微生物的判定较为困难。目前对于呼吸道感染性疾病患者病原微生物的判定需要依赖于报告解读者对于mNGS检测技术、医学微生物学、感染病学知识的了解而所积累的经验。对于责任病原微生物的判定是否有更为友好的方式也是值得深入探索的问题,有倡议建立"临床微生物测序委员会",由经验丰富的微生物专家、感染病专家和主治医师共同讨论[70]。
微生态与责任病原微生物的判定:目前对于人体微生物菌群的研究主要集中在肠道,通过调节肠道菌群治疗疾病已经有了广泛的应用(如益生菌、粪菌移植等)。呼吸道作为开放体腔,定植大量微生物,其微生态也与人类的健康息息相关,已有部分研究证实呼吸道微生态与肺部感染及预后存在相关性,并提出了一些潜在的预后相关的微生物标记物[71]。但目前对于呼吸系统微生态的认识仍然不够深入。借助mNGS检测过程中获得的肺部微生态信息,是否能够辅助判断患者是否发生感染,甚至辅助提示责任病原微生物,有待进一步的探索与研究。
宿主免疫应答与责任病原微生物判定:在对呼吸道标本mNGS检测过程中,RNA检测流程除了能检测到微生物的转录本信息,同时也可以获得宿主的转录组信息,通过对宿主转录信息的挖掘,尤其是与免疫相关的基因通路的研究,借助mNGS所产生的大量数据,有助于加深对肺部感染的理解。已有研究发现了部分与特定病原微生物感染及预后相关的宿主差异表达基因[9,72]。但目前仍然缺乏系统的临床研究数据。
宏转录组与责任病原微生物判定:RNA病毒在呼吸道感染中占据重要地位,因此对于不排除病毒感染的患者进行mNGS检测时,同时进行DNA及RNA的检测较为必要。除了RNA病毒外,DNA生物的转录本也能通过RNA流程被检测到。因此,DNA与RNA检测流程的结果可以对DNA微生物的存在进行相互验证,进一步提高检出结果的可信度。同时,责任病原微生物相较于定植微生物生命活动可能更为活跃而产生更多的转录本[73]。呼吸道标本由于存在大量的定植微生物,责任病原微生物的认定一直较为困难,通过RNA检测流程辅助责任病原微生物认定值得进一步探索。
编委会成员名单(以下名单按姓氏首字母顺序排列,排名不分先后):
陈佰义 中国医科大学附属第一医院感染病科
陈 宏 哈尔滨医科大学附属第二医院呼吸与危重症医学科
高晓东 复旦大学附属中山医院感染管理科
胡必杰 复旦大学附属中山医院感染病科
黄建荣 浙江大学医学院附属第一医院感染病科
黄 茂 南京医科大学第一附属医院(江苏省人民医院)呼吸与危重症医学科
黄 怡 海军军医大学第一附属医院呼吸与危重症医学科
金文婷 复旦大学附属中山医院感染病科
赖国祥 中国人民解放军联勤保障部队第九〇〇医院呼吸内科
李 娜 复旦大学附属中山医院感染病科
吕晓菊 四川大学华西医院感染性疾病中心
马筱玲 中国科学技术大学附属第一医院检验科
缪 青 复旦大学附属中山医院感染病科
倪语星 上海交通大学医学院附属瑞金医院临床微生物科
潘 珏 复旦大学附属中山医院感染病科
逄崇杰 天津医科大学总医院感染免疫科
彭 劼 南方医科大学南方医院感染内科
沙 巍 上海市肺科医院结核科
施 毅 南京大学医学院附属金陵医院呼吸与危重症医学科
时国朝 上海交通大学医学院附属瑞金医院呼吸与危重症科
宋元林 复旦大学附属中山医院呼吸科
孙自镛 华中科技大学同济医学院附属同济医院检验科
王明贵 复旦大学附属华山医院抗生素研究所
王晓辉 四川大学华西医院感染内科
吴文娟 同济大学附属东方医院检验科
谢俊刚 华中科技大学同济医学院附属同济医院呼吸与危重症科
解立新 中国人民解放军总医院呼吸与危重症医学部
徐英春 北京协和医院检验科
杨 帆 复旦大学附属华山医院抗生素研究所
杨文杰 天津市第一中心医院感染科
杨 阳 四川省人民医院呼吸科
叶 枫 广州医科大学附属第一医院呼吸内科
俞云松 浙江大学医学院附属邵逸夫医院感染科
张建初 华中科技大学同济医学院附属协和医院呼吸科
赵 立 中国医科大学附属盛京医院呼吸科
郑 波 北京大学临床药理研究所
郑 昕 华中科技大学同济医学院附属协和医院感染科
卓 超 广州医科大学附属第一医院感染科
执笔:
金文婷 复旦大学附属中山医院感染病科
方圆、徐卓菲、蔡青青、洪登伟[探因医学技术(浙江)有限公司]对检测流程、技术特点以及结果影响因素的探讨与建议
所有作者均声明不存在利益冲突



























